Estructura general del ADN Introducción a la replicación · PDF file1-Estructura...
Transcript of Estructura general del ADN Introducción a la replicación · PDF file1-Estructura...

Estructura general del ADN Introducción a la replicación
CLASE 5:
Profesora: Carmen Gloria Fuentealba Jara Email. [email protected]; [email protected]
Unidad I: GENOMA Y ORGANISMO

1-Estructura General del ADN 2-Genes específicos 3-Proceso de replicación y regulación enzimática de la expresión génica
Objetivos y aprendizajes esperados


Introducción a la replicación

Helicasas: Romper los puentes de hidrógeno de la doble hélice permitiendo el avance de la horquilla de replicación.

Topoisomerasas impide que el ADN se enrede debido al superenrollamiento producido por la separación de la doble hélice (renaturalice).
Proteínas SSB (single-stranded DNA binding proteins) impide
que la hebra se enrolle consigo misma.

ADN Polimerasas Sintetiza la cadena complementaria de forma continua en la hebra adelantada y de forma discontinua en la hebra rezagada Rellenar espacios de los fragmentos OKAZAKI

ADN Polimerasas Sintetiza la cadena complementaria de forma continua en la hebra adelantada y de forma discontinua en la hebra rezagada Rellenar espacios de los fragmentos OKAZAKI

ADN Polimerasas Sintetiza la cadena complementaria de forma continua en la hebra adelantada y de forma discontinua en la hebra rezagada Rellenar espacios de los fragmentos OKAZAKI

ARN Primasa La sintetiza el cebador de ARN necesario para la síntesis de la cadena complementaria a la cadena rezagada.
ADN Ligasa une los fragmentos de Okazaki

PRIMER CEBADOR o PARTIDOR
Pequeñas piezas de ADN que anillan a secuencias específicas ej. el 27Forward y el 1525 Reverse, Una vez que los "primers" se anillan la ADN polimerasas extiende
e ADN desde el extremo 5' hasta el 3' final.
27F:AGAGTTTGATCMTGGCTCAG.

Numero de genes específicos
Especie Nº genes
Ser humano (Homo sapiens) 20.500
Pulga de agua (Daphnia pulex) 31.000
Ratón (Mus musculus) 23.000
Bacteria E. coli 4.377
Arroz (Oryza sativa) 28.000
Levadura (S. cerevisiae) 5.800
Mosca (Drosophila melanogaster) 17.000
Gusano (C. elegans) 21.733
Arabidopsis (A. thaliana) 25.500
Perro (Canis lupus) 19.300

Numero de genes específicos
Especie Nº genes
Ser humano (Homo sapiens) 20.500
Pulga de agua (Daphnia pulex) 31.000
Ratón (Mus musculus) 23.000
Bacteria E. coli 4.377
Arroz (Oryza sativa) 28.000
Levadura (S. cerevisiae) 5.800
Mosca (Drosophila melanogaster) 17.000
Gusano (C. elegans) 21.733
Arabidopsis (A. thaliana) 25.500
Perro (Canis lupus) 19.300

ADN
MITOCONDRIAL
Genes de importancia evlutiva
-Citocromo Oxidasa I y Cit b -Origen Materno -ADN circular -Alta tasa de Mutación -Codifica dos ARN ribosómicos, -22 ARN de transferencia y 13 proteínas que participan en la fosforilación oxidativa.

El ADN mitocondrial codifica 13 proteínas involucradas en la producción de energía celular y procesos de fosforilación oxidativa. Por lo tanto, el entorno que rodea la mitocondria y el ADN mitocondrial está expuesto al daño oxidativo producido por los radicales libres generados en ese metabolismo.
Si a esto se le añade el hecho de que el material genético de las mitocondrias no está protegido por histonas como lo está el ADN nuclear, y que los mecanismos de reparación de daños el ADN son poco eficientes en las mitocondrias, obtenemos como resultado que la tasa de mutación aumenta hasta ser 10 veces mayor que la del genoma nuclear

Filogenias basadas en Cyt-b
Nuestros mejores amigos son los lobos. Un estudio filogenético de 736 pb del gen mitocondrial Citocromo b demostró que los lobos divergen de los perros en un 0.2% de sus bases, de los coyotes en un 4% y de los zorros en un 17%. Por estas razones, en 1993 la designación Canis familiaris fue cambiada a Canis lupus familiaris
Arbol filogenético y árbol genealógico

Filogenia basada en COI


GEN ITS ADN Ribosomal (nuclear) no codifica sujetoa continua mutación ( tasa constante).
Alta tasa de mutación no afectado por las reparasas.
Los ribosomas son diferentes en procariontes y eucariontes


RESUMEN CLASE 5
Estructura ADN Función de H-H Enlaces Fosfodiester
Replicación en Eucariontes Regulación enzimática
Helicasas
Topoisomerasas
Proteínas SSB
ARN Primasa
ADN Polimerasas
Genes de Importancia evolutiva
F U N C I O N
ITS COI
Cyt-b

Cultivo bacteriano en placa Petri
Unidad II: GENOMA Y ORGANISMO
Clase 6: Replicación en Procariontes

Objetivos y aprendizajes esperados 1-Conocer el proceso replicativo en procariontes 2-Relacionar comparativamente con el proceso replicativo de eucariontes 3-Estructura modelo operon de Procariontes. 4-Función de los intrones y exones 5- Introducción síntesis proteica
5 de Mayo 2014

Caracteristicas de la replicación en procariontes
La replicación del ADN sigue los mismas etapas tanto en procariotas como en eucariotas.
En ambos es semiconservativa y bidireccional, cadenas en horquillas separadas, se necesitan cebadores, se sintetizan las nuevas cadenas mediante polimerasas, etc.
Pero debido a las diferencias estructurales entre los cromosomas de procariotas y eucariotas y su bioquímica diferente, el proceso y las enzimas son también un poco diferentes.

En las bacterias existe un solo origen de replicación, al que llamamos Ori C. Ya que el ADN procariota es una única molécula circular, a partir de este único punto, la replicación avanza en ambas direcciones hasta que se replique toda la molécula.
El cromosoma entero es un replicón. Cuando la duplicación se esta llevando a cabo podemos observar los llamados ojos o burbujas de replicación
1- Replicación
1er Indiv.
2do Indiv.

Los fragmentos de Okazaki son más largos, y la velocidad de elongación mas rápida.
Las ADN polimerasas solo sintetizan en el sentido 5' - 3'.
Existen 3 tipos de ADN polimerasas I,II y III.
Las tres se encargan de la elongación y reparación, sin embargos solo una una se encarga de corregir ADN pol I.

Reparación y corrección
Covalente??????
Enzimas requeridas para la replicación de procariontes

2-Estructura génica y organización
Los genes de las bacterias y de los organismos superiores se diferencian en su organización. Esto es debido a que el genoma bacteriano es muy pequeño y debe reducir la información al mínimo posible.
Al revés el genoma en mamiferos es tan amplio que se dice que solo el 10% posee genes, así que muchas regiones no codificantes rodean a los genes e incluso estáN dentro de ellos INTRONES y EXONES (regiones codificantes) que luego se arreglan en el splicing.
Cual esta sujeto a mutaciones?????? Porque???????

Organización genes eucariontes: gen para Ovoalbumina


Organización genes procariontes
No existen intrones

DNA
RNA polimerasa
ADN Bacteriano Componentes de un
operón
P: promotor de los genes estructurales E1, E2, E3 y E4 R: gen regulador (codifica una proteína represora que regula la transcripción de los genes estructurales) O: operador (secuencia reconocida por la proteína represora que impide la transcripción) Un operón es un conjunto de genes, localizados contiguamente en el DNA, que obedece a las mismas señales de encendido o apagado.

Los operones están formados por genes estructurales y una región de control
Galactosidasa Permeasa Transacetilasa


s
procarionte
Diferentes tasas de sedimentación S por centrifugación
Proteinas
Diferencias entre el ribosoma eucarionte y procarionte

Recordar:
Proteína : Conjunto de aminoácidos que forman una cadena polipeptidica.
Triplete de codones
aminoacidos
Cadena Polipeptidica =proteinas
Las proteínas están formadas por ácido ribonucleico (ARN).


SINTESIS DE PROTEINAS:
TRANSCRIPCIÓN
Clase 7
7-5-2014

T A C G A A C C G T T G C A C A T C
A U G C U U G G C A A C G U G
Transcripción:
1- Iniciación: Una ARN-polimerasa comienza la síntesis del precursor del ARN
l( base de la futura proteina) a partir de "secuencias de consenso " que se
encuentran en el ADN antes de ser ARN precursor. Completa con Uracilo.
ARNpolimerasa
PROMOTOR
ADN
ARN


A U G C U C G U G
Transcripción:
3- Finalización: Una vez que la enzima (ARN polimerasa) llega a la región de
termino del gen, finaliza la síntesis del ARN. Entonces, una poliA-polimerasa
añade una serie de nucleótidos con adenina, la cola poliA, y el ARN, llamado
ahora ARNm precursor, se libera.
m-GTP
poliA-polimerasa
U A G A A A A A
ARNm precursor
región de termino

AAAAAA AUG UAG
cola
4. Maduración (cont.): El ARNm precursor contiene tanto exones como intrones. Se
trata, por lo tanto, de un ARNm no apto para que la información que contiene sea
traducida y se sintetice la correspondiente molécula proteica. En el proceso de
maduración un sistema enzimático reconoce, corta y retira los intrones y las
ARN-ligasas unen los exones, formándose el ARNm maduro.
Cabeza
ARN maduro sin intrones bases agrupados en tripletes
de codones

Región codificadora del gen
Promotor E1 I1 E2 I2 E3 Terminador
ADN
ARNm
precursor
ARNm maduro
AAAAAA
AAAAAA
AUG UAG
AUG UAG
ATC TAC
Cabeza
Cabeza E1 I1 E2 I2 E3 cola
cola
Maduración del ARNm (Visión de conjunto).
ETAPA I

SINTESIS DE PROTEINAS:
TRADUCCIÓN
ETAPA II
Síntesis proteica = Lectura de codigo
Etapa en la que se une el ARNm (maduro) al ribosoma y los codones son traducidos en aminoacidos. Iniciación
12 fases de elongación Finalización
ENZIMAS: ARN Transferencia

1er aminoácido
ARNt Anticodón
Codón
ARNm
Subunidad menor del ribosoma
AAAAAAAAAAA P A
A U G C A A
U A C
Iniciación: La subunidad pequeña del ribosoma se une a la región líder del ARNm(m) y
este se comienza a leer desde el codón AUG, que codifica el principio de la proteína (UAC).
Se les une entonces el complejo formado por el ARNt-metionina (Met). La unión se produce
entre el codón del ARNm y el anticodón del ARNt que transporta la metionina (Met).
5’ 3’
U G C U U A C G A U A G
(i)
ARNt Transportar los aminoacidosAl complejo ribosoma ARNm(m) formando el anticodon (proteína). Traducido a Metionina
ARNm(m)
Proteina

Subunidad menor del ribosoma
AAAAAAAAAAA P A
A U G C A A
U A C
Elongación I: A continuación se une la subunidad mayor a la menor completándose el
ribosoma. El complejo ARNt-aminoácido2 , la glutamima (Gln) [ARNt-Gln] se sitúa enfrente
del codón correspondiente (CAA). La región del ribosoma a la que se une el complejo ARNt-
Gln se le llama región aminoacil (A).
5’ 3’ G U U
U G C U U A C G A U A G
(i)
Región aminocil A, se une la otra subunidad
Gln Triplete codones

ARNm AAAAAAAAAAA
P A
A U G C A A
U A C
Elongación II: Se forma el enlace peptídico entre el grupo carboxilo de la metionina (Met)
y el grupo amino del segundo aminoácido, la glutamina (Gln).
5’
G U U U G C U U A C G A U A G
3’

AAAAAAAAAAA P A
A U G C A A
Elongación III: El ARNt del primer aminoácido, la metionina (Met) se libera.
5’
G U U U G C U U A C G A U A G
ARNm 3’
Los ARNt se liberan

AAAAAAAAAAA P A
A U G C A A
Elongación III: El ARNt del primer aminoácido, la metionina (Met) se libera.
5’
G U U U G C U U A C G A U A G
ARNm 3’

AAAAAAAAAAA P A
A U G C A A
Elongación IV: El ARNm se traslada, de tal manera que el complejo ARNt-Gln-Met queda
en la región peptidil del ribosoma, quedando ahora la región aminoacil (A) libre para la
entrada del complejo ARNt-aa3
5’ 3’
G U U U G C U G C U U A C G A U A G
ARNm

AAAAAAAAAAA P A
A U G C A A
Elongación V: Entrada en la posición correspondiente a la región aminoacil (A) del
complejo ARNt-Cys, correspondiente al tercer aminoácido, la cisteína (Cys).
5’
G U U U G C U G C U U A C G A U A G
ARNm 3’
A C
G
Los nombre de los complejos que se forman dependen del aminoacido unido al ARNt.

AAAAAAAAAAA P A
A U G C A A
Elongación VI: Unión del péptido Met-Gln (Metionina-Glutamina) a la cisteína (Cys).
5’
G U U U G C U G C U U A C G A U A G
ARNm 3’
A C G

AAAAAAAAAAA P A
A U G C A A
Elongación VI: Unión del péptido Met-Gln (Metionina-Glutamina) a la cisteína (Cys).
5’
G U U U G C U G C U U A C G A U A G
ARNm 3’
A C G

AAAAAAAAAAA P A
A U G C A A
Elongación VII: Se libera el ARNt correspondiente al segundo aminoácido, la glutamina
(Glu).
5’
U G C U G C U U A C G A U A G
ARNm 3’
A C G
(i)

AAAAAAAAAAA P A
A U G C A A
Elongación VIII: El ARNm corre hacia la otra posición, quedando el complejo ARNt3-Cys-
Glu-Met en la región peptidil del ribosoma.
5’
U G C U G C U U A C G A U A G
ARNm 3’
A C G

AAAAAAAAAAA P A
A U G C A A
Elongación IX: Entrada del complejo ARNt-Leu correspondiente al 4º aminoácido, la
leucina.
5’
U G C U G C U U A C G A U A G
ARNm 3’
A C G
A A U
Leu

AAAAAAAAAAA P A
A U G C A A
Elongación X: Este se sitúa en la región aminoacil (A).
5’
U G C U G C U U A C G A U A G
ARNm 3’
A C G A A U

AAAAAAAAAAA P A
A U G C A A
Elongación XI: Unión del péptido Met-Gln-Cys con el 4º aminoácido, la leucina (Leu).
Liberación del ARNt de la leucina. El ARNm se desplaza a la 5ª posición
5’
U G C U G C U U A C G A U A G
ARNm 3’
A A U

AAAAAAAAAAA P A
A U G C A A
Elongación XII: Entrada del ARNt de la leucina, el 5º aminoácido, la arginina (ARNt-Arg).
5’
U G C U G C U U A C G A U A G
ARNm 3’
A A U
G C U

AAAAAAAAAAA P A
A U G C A A
5’
U G C U U A C G A U A G
ARNm 3’
Arg-Leu-Cys-Gln-Met
G C
U
Finalización I: Liberación del péptido o proteína. Las subunidades del ribosoma se
disocian y se separan del ARNm.

AAAAAAAAAAA
Finalización II: Después unos minutos los ARNm son digeridos por las enzimas del
hialoplasma.
5’
ARNm
3’
A U G C A A U G C U U A C G A U A G
(i)
Resultado final una proteína en el citoplasma.

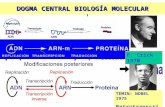
ADN ARN
Transcripción
ARN :Azucar ribosa Timina por Uracilo Cadena sencilla
Citoplasma
RECORDAR: Síntesis proteica
ARN-Polimerasa
ARN molde ARN mensajero
Transducción
ARN maduro
Proteína

X e Y

X e Y